Реверс-инжиниринг и эволюция
Современная криптография и информационная безопасность традиционно оперируют кремниевыми системами, однако наиболее сложные и защищенные протоколы передачи информации были созданы природой за миллиарды лет до появления первого транзистора.
Данный доклад предлагает рассматривать живую клетку не как аморфный биологический объект, а как высокоорганизованную вычислительную среду, исполняющую закрытый код, оптимизированный в ходе эволюционной гонки.
Если рассматривать геном как скомпилированный бинарный файл, а клетку — как среду выполнения (runtime), то методы современной молекулярной биологии и микроскопии предстают в совершенно ином свете: как инструменты статического и динамического анализа, а средства РНК-терапии — как инструменты «горячего патчинга» системы.
Реверс-инжиниринг и эволюция
Слайд 1: Введение — Почему реверс-инжиниринг?
Представьте: у вас есть загадочная программа, которая работает, но вы не знаете, как. Вы не можете просто спросить автора — приходится разбирать её по частям. Это реверс-инжиниринг в IT. А теперь представьте, что такая "программа" — это живая клетка человека. Она эволюционировала миллиарды лет, и её "код" (ДНК) полон секретов. В этом докладе мы увидим, как методы из IT помогают исследовать клетку, чтобы понять жизнь. Почему это актуально? Потому что от понимания клетки зависят лекарства, лечение рака и даже синтетическая биология. Переходим к основам IT-подходов, чтобы на их примере показать аналогии с биологией.
Слайд 2: Обзор подходов к реверс-инжинирингу в IT
В IT реверс-инжиниринг — это искусство разбирать софт без исходного кода. Давайте разберём по шагам, почему эти методы работают и как они связаны.
Статический анализ: Здесь мы смотрим на код "в покое", без запуска. Инструменты вроде IDA Pro или Ghidra разбирают бинарный файл на инструкции, строят графы потоков управления (где видно, как функции вызывают друг друга) и находят кросс-ссылки (связи между частями кода). Это как читать книгу: вы видите структуру, но не знаете, как она "оживёт". Полезно для быстрого обзора, но не показывает, что происходит в реальности.
Динамический анализ: Теперь запускаем программу в отладчике, типа GDB или WinDbg. Устанавливаем точки останова (паузы на ключевых моментах), трассируем выполнение (записываем каждый шаг) и наблюдаем, как меняются регистры (временные хранилища данных) и память. Это даёт живое понимание: почему программа крашится или как она обрабатывает input.
Логирование и мониторинг: Чтобы поймать скрытое, вставляем "хуки" (перехватчики) или используем MITM (man-in-the-middle) — как прокси, который записывает все события. Это критично, когда статический анализ упускает динамику, а динамический — слишком хаотичен.
Почему от статического к динамическому? Статический даёт карту, динамический — путешествие по ней. Вместе они строят полную картину. Теперь представьте: а если применить это к клетке? Переходим к аналогиям, чтобы показать, как IT-логика переносится на биологию.
Слайд 3: Аналогия — Клетка как компьютер
Клетка — это не просто мешок с химией, а сложная вычислительная машина. Почему такая аналогия? Потому что она упрощает: в IT мы разбираем неизвестный код, в биологии — неизвестные процессы. Давайте разберём.
ДНК как программа: ДНК — это "бинарный код" клетки, последовательность нуклеотидов, которая диктует, как строить белки. Рибосомы — "компилятор", переводящий этот код в исполняемые белки. Органеллы (митохондрии, ядро) — как модули процессора: каждый обрабатывает свою задачу.
Входы-выходы: Как в реверс-инжиниринге ПО, где мы подаём input и смотрим output, в клетке мы стимулируем (например, лекарством) и наблюдаем реакцию. Это помогает вскрыть "чёрный ящик" без полного знания "кода".
Эволюция как оптимизатор: Эволюция "пишет" этот код веками, добавляя резервные системы и переиспользуя части — как умный программист, который делает код отказоустойчивым.
Эта аналогия мостик: от IT к биологии, потому что клетки, как программы, имеют структуру (статическую) и поведение (динамическое). Теперь применим статический анализ к клетке.
Слайд 4: Статический анализ клетки — Взгляд на структуру
В IT статический анализ — это разбор кода без запуска. В биологии — "заморозка" клетки для изучения. Почему сначала статический? Он даёт базу, как каркас дома перед осмотром комнат.
Крио-электронная микроскопия (Cryo-EM): Образец замораживают в жидком азоте, чтобы сохранить молекулы в естественном состоянии. Электроны дают разрешение до 1-2 ангстрем (0.1 нм), показывая 3D-структуры белков и органелл. Это как IDA Pro для клетки: строит "графы" молекулярных взаимодействий.
Chan Zuckerberg Biohub: Этот институт развивает cryo-EM томографию для мультимасштабной визуализации — от атомов до органов. Они создают атласы, как 3D-карты эмбрионов рыб, где цвета показывают активные гены. Почему важно? Потому что инвестиции (сотни миллионов) ускоряют открытия.
Переход к динамическому: статический даёт снимок, но жизнь — движение. Нужно видеть процессы в реальном времени.
Слайд 5: Динамический анализ клетки — Наблюдение за жизнью
В IT динамический анализ — запуск с отладкой. В биологии — слежка за клеткой "вживую". Но здесь проблемы: масштабы крошечные, а наблюдение может убить объект.
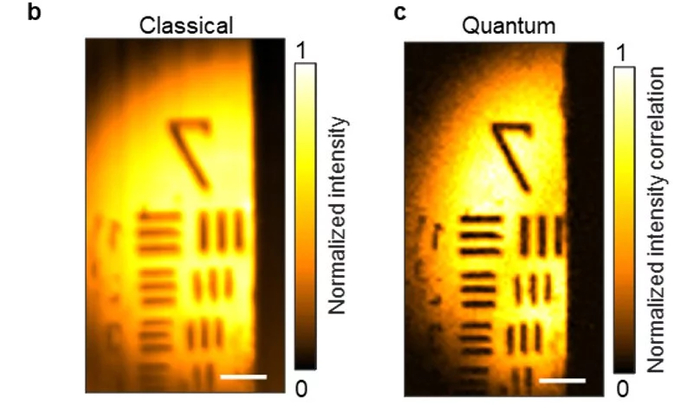
Проблемы с традиционной микроскопией: Оптическая даёт реальное время, но разрешение 350-700 нм — молекулы (0.1-1 нм) не видно. Флуоресцентные метки токсичны: ультрафиолет повреждает ДНК, вызывая апоптоз (самоуничтожение клетки). Наблюдение меняет наблюдаемое — как в квантовой механике.
Решение: Рамановская спектроскопия: Свет рассеивается от электронных облаков молекул, не возбуждая их (неинвазивно). Вода прозрачна для этого, так что сигнал чистый. Конфокальная версия фокусируется на точке, игнорируя помехи от соседних молекул.
Почему от проблем к решению? Чтобы показать эволюцию методов: от разрушительных к щадящим.
Слайд 6: Современные методы динамического анализа
Углубляемся: от базовой рамановской к продвинутым, потому что технологии эволюционируют, как и клетки.
Гиперспектральная микроскопия (SRS/CARS): Многоканальная, без меток — ловит спектры белков, липидов. Horiba системы сочетают рамановский с тёмнопольным освещением: сначала находишь объект, потом сканируешь.
Центры коллективного пользования (ЦКП): В России (МГУ, ИТМО) доступны такие микроскопы. Открытые датасеты: "Раман-карта клетки" (спектры органелл, скачиваемые файлы как HAEC_RS_750nm.zip) или 3D-визуализации культур клеток.
Это даёт "трейс-логи" — данные о реакциях на лекарства, как в IT-отладке.
Слайд 7: Искусственная клетка-MITM и дополнительные логи
В IT MITM перехватывает трафик. В биологии — "посредник" для слежки.
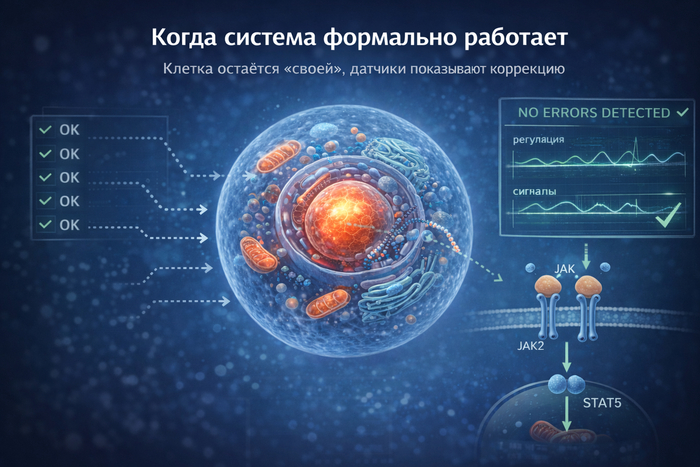
Концепция: Искусственная наносистема рядом с клеткой фиксирует pH, энергию, молекулы. Это не меняет ДНК, а "подслушивает" — как биофорензика.
Почему полезно? Даёт причинно-следственные связи, как стэк в дебагере. Без этого "код" ДНК бесполезен без контекста.
Переход к эволюции: теперь, когда мы видим, как работает, поймём, как это "написано".
Слайд 8: Эволюция как оптимизатор кода
Эволюция — "программист", тестирующий мутации. Почему здесь? Потому что анализ показывает, как код устойчив.
Оптимизация: Дубли генов — резервные копии. Мутации: случайные (рак как баг) или адаптивные (польза).
Иммунная система как антивирус: Сканирует ДНК, блокирует дефекты. Аллель-специфическая РНК-терапия: siRNA для Хантингтона — блокирует только мутант, как сигнатурный сканер.
Слайд 9: Текущая ситуация и критика подхода
Сейчас: Прогресс в AI-моделях клеток (виртуальные клетки на миллиарды данных). Но критика: Биология стохастическая (случайная), не как машина; сложность (10^14 атомов) делает полный реверс мечтой. Аналогии упрощают реальность.
Слайд 10: Заключение — К полному пониманию жизни
Собирая данные (от нуклеотидов к органам), мы "декомпилируем" жизнь. IT-инструменты + биотехнологии открывают двери к новым терапиям.
Что это дает?
Этот подход предлагает теоретический законченный фреймворк для исследований клетки — систематическую модель, где клетка трактуется как "чёрный ящик" с входами, выходами и внутренним кодом. Он объединяет статический/динамический анализ, логирование и эволюционные insights, чтобы предсказывать поведение клетки, как в IT предсказывают баги. Практически: ускоряет разработку лекарств (например, моделирование рака), синтетическую биологию (программирование клеток для производства инсулина) и понимание болезней.
Есть ли такая концепция сейчас? Да! В системной биологии есть фреймворки реверс-инженеринга, как в обзоре "Reverse engineering and identification in systems biology" (2014, обновлённые версии до 2025), где классифицируют модели от interaction-based до mechanism-based. Ближе всего — Virtual Cell framework (2025), который интегрирует данные в предиктивные модели, от симуляций до AI, для создания "виртуальных аналогов" клеток. Это уже используется в биомедицине для тестирования гипотез без экспериментов. Также в синтетической биологии клетки "программируют" как компьютеры. Но полный "законченный" фреймворк ещё развивается — критики отмечают, что биология слишком хаотична для идеальной аналогии.
Однако, фреймворк Virtual Cell (2025), представленный такими разработками, как AI Virtual Cell (AIVC) и модели вроде State института Arc Institute, в первую очередь сосредоточены на создании предсказательных, основанных на данных симуляций клеточного поведения. Для этого используются интеграция multi-omics данных и крупные нейронные сети, которые прогнозируют реакции клетки на возмущения — такие как действие лекарств или генетические изменения — позволяя проводить виртуальные эксперименты без прямого физического анализа.
В противоположность этому, предложенный подход обратного инжиниринга рассматривает клетку как «чёрный ящик», аналогично программному обеспечению. Он делает акцент на методах, вдохновлённых информационными технологиями: статическом анализе (например, крио-ЭМ) и динамическом анализе (например, рамановской спектроскопии), использовании промежуточных механизмов, напоминающих MITM-подход, для логирования параметров, а также на интерпретации эволюции как оптимизатора кода. Такой подход направлен на разбор и понимание клеточных механизмов через экспериментальные наблюдения и аналогии, а не исключительно через предсказательное моделирование.
Все это вместе может быть использовано для детального динамического изучения работы биологической клетки и полного понимания как устроена жизнь. От нуклеотидов, минимальных единиц информации в ДНК, до работы клеток, построенных рибосомами по этому коду, к тканям органов и живому человеку как целому.